ARNr 5S
O ARNr 5S (ou 5S rRNA) é un ARN ribosómico de aproximadamente 120 nucleótidos de longo cunha masa de 40 kDa, que é un compoñente estrutural e funcional da subunidade maior (de 50S) dos ribosomas de bacterias, arqueas e eucariotas, coa excepción dos ribosomas mitocondriais de fungos e animais. A denominación 5S débese a que esa é a velocidade de sedimentación da molécula nunha ultracentrífuga, medida en unidades svedberg (S).[1]
| ARNr 5S | |
|---|---|
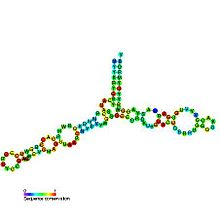 Estrutura secundaria predita e conservación de secuencia do ARNr 5S | |
| Identificadores | |
| Rfam | RF00001 |
| Outros datos | |
| Dominio(s) | Eukaryota; Bacteria; Archaea |
| GO | 0005840 0003735 |
| Estruturas PDB | PDBe |

Biosíntese
En procariotas, o xene do ARNr 5S está localizado nos operóns de ARNr e está situado augas abaixo dos xenes dos ARNr das subunidades ribosómicas maior e menor e é cotranscrito formando un precursor policistrónico.[3] Unha particularidade dos xenomas nucleares eucariotas é a presenza de múltiples copias do xene do ARNr 5S (ADNr 5S) agrupados en repeticións en tándem, cuxo número de copias varía entre especies.[4][5]O ARNr 5S eucariota é sintetizado pola ARN polimerase III, mentres que outros ARNr eucariotas son escindidos a partir dun precursor de 45S transcrito pola ARN polimerase I. En ovocitos de Xenopus observouse que os "dedos" 4-7 do factor de transcrición de nove dedos de cinc TFIIIA poden unirse á rexión central do ARNr 5S.[6][7] A unión entre o ARNr 5S e o TFIIIA serve tanto para reprimir máis transcrición do xene de ARNr 5S como para estabilizar o transcrito de ARNr 5S ata que se require para a ensamblaxe do ribosoma.[8]
Estrutura
A estrutura secundaria do ARNr 5S consiste en cinco hélices (denominadas do I ao V en números romanos), catro bucles (B-E) e unha bisagra (A), que xuntos forman unha estrutura con forma de Y. Os bucles C e D son forquitas terminais e os bucles B e E son internos.[4] Segundo estudos filoxenéticos, as hélices I e III son probablemente ancestrais.[9] A hélice III comprende dúas adenosinas conservadas.[10] A hélice V, coa súa estrutura en forquita, crese que interacciona co TFIIIA.[4]
Localización no ribosoma

Usando diversas técnicas moleculares, como a microscopia inmunoelectrónica, enlaces cruzados químicos intermoleculares e cristalografía de raios X, determinouse con gran precisión a localización do ARNr 5S dentro da subunidade ribosómica maior. En bacterias e arqueas, a propia subunidade ribosómica maior (LSU) está composta por dúas moléculas de ARNr, o ARNr 5S e o ARNr 23S, xunto con numerosas proteínas asociadas.[3] En eucariotas, a subunidade ribosómica maior contén os ARNr 5S, 5,8S e 28S e aínda máis proteínas.[12][13]A estrutura tridimensional da subunidade ribosómica maior mostra unha superficie relativamente lisa por un lado e unha superficie oposta con tres proxeccións, especialmente a protberancia L1, a protuberancia central (CP) e o talo L7/L12. A protuberancia L1 e o talo L7/L12 están dispostos rodeando laterlmente a protuberancia central. O ARNr 5S está localizado na protuberancia central e participa na formación e na estrutura desta proxección. Os outros constituíntes principais da protuberancia central son o ARNr 23S (ou alternativamente o 28S en eucariotas) e varias proteinas como L5, L18, L25 e L27.[14]
Funcións ribosómicas
A función exacta desempeñada polo ARNr 5S non está aínda clara. En Escherichia coli, as delecións no xene do ARNr 5S reducen a taxa de síntese proteica e teñen un efecto negativo máis profundo sobre as condicións reinantes na célula que as delecións dun número comparable de copias doutros xenes de ARNr (16S e 23S).[15] Os estudos cristalográficos indican que as proteínas que se unen ao ARNr 5S e outras proteínas da protuberancia central da subunidade ribosómica maior xogan un papel na unión dos ARNt.[14] Ademais, a proximidade topográfica e física entre o ARNr 5S e o 23S, que forma a peptidil trnasferase e o centro de asociación da GTPase, suxire que o ARNr 5S actúa como un mediador entre os dous centros funcionais do ribosoma ao formar, xunto coas proteínas que se unen ao ARNr 5S e outros compoñentes da protuberancia central, pontes intersubunidades e sitios de unión do ARNt.[14]
Papel na ensamblaxe dos ribosomas
En eucariotas, o ribosoma citosólico ensámblase a partir de catro ARNr e unhas 80 proteínas.[13][16] Unha vez transcrito, os extremos 3' do ARNr 5S son procesados polas exonucleases Rex1p, Rex2p e Rex3p.[4] As subunidades ribosómicas de 60S e 40S son exportadas desde o núcleo ao citoplasma, onde se unen para formar o ribosoma de 80S maduro e competente para facer a tradución de proteínas. Segue sendo moi discutido cal é o momento en que O ARNr 5S se integra no ribosoma,[4] pero acéptase en xeral que o ARNr 5S se incorpora á particula de 90S, que é a precursora da partícula de 60S, como parte dun complexo ribonucleoproteínico independente do ribosoma formado polo ARNr 5S e a proteína ribosómica L5.[16]
Interaccións con proteínas
Varias proteínas importantes que interaccionan co ARNr 5S son as seguintes:
Proteína La
A interacción do ARNr 5S coa proteína La impide a degradación do ARN por exonucleases na célula.[17] A proteína La encóntrase no núcleo de todos os organismos eucariotas e asóciase con varios tipos de ARNr transcritos pola ARN pol III. A proteína La interacciona con estes ARN (incluíndo o ARNr 5S) por medio do seu tracto de 3' oligo-uridina, colaborando na estabilidade e pregamento do ARN.[4][18]
Proteína L5
En células eucariotas, a proteína ribosómica L5 asóciase e estabiliza o ARNr 5S formando unha partícula ribonuleoproteica prerribosómica (RNP) que se encontra tanto no citosol coma no núcleo. A deficiencia de L5 impide o transporte do ARNr 5S co núcleo e ten como resultado unha diminución na ensamblaxe ribosómica.[4]
Outras proteínas ribosómicas
En procariotas o ARNr 5S únese ás proteínas ribosómicas L5, L18 e L25, mentres que nos eucariotas o ARNr 5S é só se sabe que se une á proteína ribosómica L5.[19] En Trypanosoma brucei, o axente causante da tripanosomíase africana (enfermidade do sono), o ARNr 5S interacciona con dúas proteínas que se unen ao ARN estreitamente relacionadas, a P34 e a P37, cuxa perda ten como resultado un menor nivel global de ARNr 5S.[4]
Presenza en ribosomas
| ARNr 5S | |
|---|---|
| Identificadores | |
| Rfam | RF02547 |
| Outros datos | |
| Dominio(s) | Eukaryota; |
| GO | 0005840 0003735 |
| Estruturas PDB | PDBe |

As maquinarias de tradución de proteínas das mitocondrias e plastidios (orgánulos de orixe bacteriana endosimbiótica) e os seus correspondentes bacterianos comparten moitas características, mais tamén tañen marcadas diferenzas. Os xenomas dos orgánulos codifican os ARNr das subunidades menor e maior do ribosoma sen excepción, aínda que a distribución dos xenes do ARNr 5S (rrn5) é máis desigual. O rrn5 identifícase doadamente e é común nos xenomas da maioría dos plastidios. En contraste, o rrn5 mitocondrial parecía que inicialmente estaba restrinxido a plantas e un pequeno número de protistas.[20][21] Ademais, poden identificarse algúns ARNr 5S organulares máis diverxentes só con modelos de covarianza especializada que incorporan información sobre o nesgo pronunciado na composición de secuencia e variación estrutural.[22] Esta análise localiza xenes de ARNr 5S adicionais non só en xenomas de mitocondrias da maioría das liñaxes de protistas, senón tamén en xenomas de certos apicoplastos (plastidios non fotosintéticos de protozoos patóxenos como Toxoplasma gondii e Eimeria tenella).

Os ARNr 5S mitocondriais da maioría das estramenopiles comprenden a maior diversidade de estruturas secundarias.[22] Os ARNr 5S mitocondriais permutados das algas pardas representan o caso menos convencional, no que a hélice I de peche, que normalmente une os extremos 5' e 3' da molécula, é substituída por unha forquita (pechada) que orixina como resultado unha unión de tres vías aberta.
As probas existentes actualmente indican que o ADN mitocondrial de só uns poucos grupos, singularmente os animais, fungos, alveolados e euglenozoos carece do xene.[22] A protuberancia central, que normalmente está ocupada polo ARNr 5S e as súas proteinas asociadas (ver Figura 2), foi remodelado de varios xeitos. Nos ribosomas mitocondriais fúnxicos, o ARNr 5S é substituído por secuencias de expansión do ARNr da subunidade maior.[23] En cinetoplástidos (euglenozoos), a protuberancia central está formada enteiramente por proteínas do ribosoma mitocondrial evolutivamente novas.[24] Finalmente, os ribosomas mitocondriais animais incorporaron un ARNt mitocondrial específico para substituír o ARNr 5S perdido.[25][26]
Notas
Véxase tamén
Ligazóns externas
- Páxina para o 5S ribosomal RNA en Rfam
- 5SDataArquivado 27 de abril de 2010 en Wayback Machine.
- 5S Ribosomal RNA Medical Subject Headings (MeSH) na Biblioteca Nacional de Medicina dos EUA.